Consulenza genetica
La consulenza genetica è comunicazione informata ed appropriata
Per essere informata deve partire dall’individuazione di un difetto
genetico in un paziente e dal calcolo del rischio per gli altri
componenti della famiglia
Per poter essere appropriata deve saper stabilire un rapporto di
fiducia e di confidenza senza essere direttiva, cioè non deve
indirizzare la famiglia verso un unico obiettivo, ma lasciare libertà di
valutazione e di scelta
La consulenza genetica può riguardare:
1. la diagnosi di una malattia genetica clinicamente manifesta
2. il rischio riproduttivo di una coppia in epoca preconcezionale
3. la diagnosi prenatale
4. la predizione di una malattia genetica futura
5. la suscettibilità genetica
Consulenza genetica
distinguiamo due grandi categorie di patologie genetiche:
1) monoalleliche, dovute alla mutazione di una sola copia del DNA
2) bialleliche, dovute a mutazioni di entrambe le copie del DNA
•
patologie a penetranza completa (in genere disordini mendeliani)
•
a penetranza incompleta, o addirittura “circoscritta”.
La consulenza genetica cerca di stabilire quali membri della famiglia sono
interessati ed eventualmente quali possono essere portatori, e quindi
calcolare la probabilità di ogni altra persona nella famiglia (anche non
ancora nata) di essere un portatore o di ereditare la malattia
rischio riproduttivo generale
per una coppia per cui l’anamnesi personale e
familiare abbiano escluso un incremento del
rischio rispetto alla popolazione è
• 3-5% in caso di difetti congeniti rilevabili alla
nascita (anomalie cromosomiche 0.65%)
• 8-10% rilevabili entro i 10 anni di età
Durante la mitosi:
ciascun cromosoma si duplica
producendo due copie identiche:
i cromatidi fratelli.
I cromatidi restano associati
mediante il centromero.
cromatidi fratelli
• le copie si separano.
• ciascuna copia migra
in una cellula
centromero
LE FASI DELLA
MITOSI
• Interfase
• Profase
• Metafase
• Anafase
• Telofase
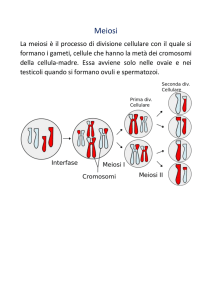
meiosi
• La meiosi è il processo che porta alla formazione
dei gameti
• I gameti sono cellule aploidi: hanno la metà dei
cromosomi delle cellule diploidi
• 23 è il numero di cromosomi dei gameti
• 46 è il numero di cromosomi di ogni altra cellula
umana
• La meiosi consiste in due divisioni cellulari
meiosi I (riduzionale) e meiosi II (equazionale)
che producono quattro cellule aploidi
meiosi
Meiosi I
Replicazione del DNA
46 cromosomi
92 Cromatidi / 92 dsDNA
Divisione riduzionale
separazione delle coppie di cromosomi
23 cromosomi
46 cromatidi / 46 dsDNA
Meiosi II
Separazione dei cromatidi
23 cromosomi
23 cromatidi / 23 dsDNA
Meiosi I
46 cromosomi
92 Cromatidi /
92 dsDNA
1.
2.
3.
4.
Profase I: ciascun cromosoma si duplica e le due parti restano
strettamente associate. Questi sono chiamati cromatidi fratelli. Il
crossing-over avviene in questa fase
Metafase I: I cromosomi omologhi si allineano al piano equatoriale
Anafase I: Le coppie omologhe si separano e i cromatidi fratelli restano
uniti
Telofase I: le due cellule figlie contengono solo un cromosoma di
ciascuna coppia
meiosi I, profase I
• Leptotene
– i cromosomi si rendono visibili
• Zygotene
– le coppie di cromosomi omologhi formano le tetradi
• Pachitene
– crossing over
• Diplotene
– i cromosomi iniziano a separarsi ma sono tenuti insieme
dai chiasmi
• Diacinesi
– ulteriore accorciamento dei cromosomi omologhi
Meiosi II
23 cromosomi
23 cromatidi /
23 dsDNA
1. Profase II: il DNA delle due cellule figlie non si replica.
2. Metafase II: i cromosomi si allineano al piano equatoriale
3. Anafase II: I centromeri si dividono e i cromatidi fratelli
migrano separatamente a ciascun polo
4. Telofase II: la seconda divisione cellulare è completa.
Quattro cellule figlie aploidi (23) sono ottenute
Spermatogonium
Oogonium
Primary
spermatocyte
Primary
oocyte
Secondary
spermatocytes
Secondary
oocyte
Gametogenesi
Polar Body I
4 spermatids
Polar Body II
Fertilized Ovum
4 spermatozoa
Oogonium
spermatogonio
Per tutta la vita
Mitosi alla pubertà
Primary
oocyte
spermatocita
primario
maschio
spermatocita
Secondario
Meiosi
in
Secondary
oocyte
64gg
Polar Body I
4 spermatidi
Polar Body II
Fertilized Ovum
4 spermatozoi
Periodo fetale
Oogonio
Mitosis
alla nascita o prima
Meiosi in progress
dopo la nascita
Si arresta al
diplotene
della meiosi I
oocita primario
dopo la pubertà
femmina
Meiosi I
completa
oocita secondario
e corpo polare I
Si arresta alla
metafase II
Alla fertilizzazione
Meiosi II
completa
Fertilized Ovum
& Polar body II
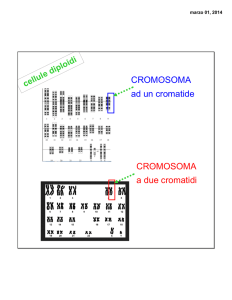
Cromosomi (corpi colorati)
• durante il ciclo cellulare i cromosomi
replicano e si formano due cromatidi
fratelli tenuti insieme dal centromero
• braccio corto = p (petit)
• braccio lungo = q (lettera successiva)
citogenetica di routine
da linfociti
sono rappresentativi di ciascun altra cellula del corpo
citogenetica prenatale
• da amniociti
• da villi coriali
• dovrebbero essere
rappresentativi delle
cellule del feto
• difficili da ottenere
Cromatina (DNA+proteine)
• Eucromatina - meno condensata contiene il DNA
codificante
• Eterocromatina - più condensata non contiene DNA
codificante, ma solo DNA non codificante
• Telomeri - cappucci all’estremità dei cromosomi che
comprendono ripetizioni multiple della sequenza
TTAGGG
• Centromeri - regioni specializzate di DNA che forniscono
il sito di ancoraggio del fuso mitotico
Eucromatina ed eterocromatina
Tecnica
Procedura
Banding pattern
bandeggio G
Proteolisi limitata seguita dalla
colorazione Giemsa
Le bande scure sono ricche in AT
Le bande chiare sono ricche in GC
bandeggio R
denaturazione al calore seguita
dalla colrazione con Giemsa
Le bande scure sono ricche in GC
Le bande chiare sono ricche in AT
bandeggio Q
digestione enzimatica e
colorazione con un colorante
fluorescente, cioè la Quinacrina
Le bande scure sono ricche in AT
Le bande chiare sono ricche in GC
bandeggio C
denaturazione con idrossido di
bario e poi colorazione con
Giemsa
Le bande scure sono ricche in
eterocromatina costitutiva
Colorazione dei
cromosomi con
coloranti specifici
per regioni ricche in
AT
o in
GC
• metacentrici, se il centromero è centrale 1, 2, 3, 16, 17, 18, 19
• submetacentrici, se il centromero non è centrale e non è vicino
ad un’estremità 4, 5, 6, 7, 8, 9, 10, 11, 12, 20, X, Y
• acrocentrici, se il centromero è vicino ad un’estremità 13, 14, 15,
21, 22
CCDS IDs per chromosome
Chromosome
Count
1
2,513
2
1,548
3
1,299
4
898
5
1,028
6
1,236
7
1,094
8
807
9
921
10
971
11
1,509
12
1,240
13
385
14
749
15
711
16
967
17
1,370
18
350
19
1,616
20
672
21
282
22
530
X
967
Y
53
XY
23
Eteromorfismi citogenetici
•
Variazione
pericentromerica del
crom. 9 9qh+
•
Inversione 9 inv
•
Variazione + inversione
Ereditarietà della variazione
pericentromerica del cromosoma 1
Le alterazioni cromosomiche sono
più frequenti al crescere dell’età
materna, mentre le mutazioni
puntiformi sono legate al numero di
divisioni cellulari che avvengono circa
ogni 15 gg nella linea germinale
maschile
tritest interpretazione dei risultati
anomalia
fetale
NTD =difetti del
tubo neurale*
AFP
Beta hCG
Alfa-feto
proteina
Normale
Trisomia
21
Trisomia
18
* NTD: anencefalia, spina bifida and encefalocele
uE
estriolo non
coniugato
Normale
Il duotest (double screen) include la valutazione del PAPP-A
(Pregnancy Associated Plasma Protein A) e la frazione libera della
gonadotropina corionica (free-betaHCG).
Viene effettuato tra la 10ma e la 13ma settimana di gravidanza dal
siero della gestante
Translucenza
nucale
free-bHCG
PAPP-A
Trisomia 21
++
++
-
Trisomia 13,18
+++
--
--
S. di Turner
++++
+/-
-
Triploidia
materna
+/-
----
---
Triploidia
paterna
+++
++++
+/-
Patologia fetale
NTD - AFP solo
Trisomia 21 - Tritest
Trisomia 18 - Tritest
Sensibilità
75-80% spina bifida
95%
anencefalia
70% Down sindrome
80% sindrome di
Edward
Anomalie ecografiche maggiori
90
80
70
60
50
40
30
20
10
0
rischio di aneuploidia
idrope <17 settimane
igroma cistico
canale A-V
oloprosencefalia
onfalocele
idrope >24 settimane
difetti cardiaci
atresia duodenale
ostruzione vescicale
Ernia diaframmatica
Arti più corti
Idrocefalo
Piede torto
Schisi facciale
ecografia
• “segni minori”
ispessimento plica nucale
valore predittivo (%)
6
5
Echogenic bowel
4
femore corto
3
focus ecogeno intracardiaco
2
1
pielectasia renale
0
donne a basso donne ad alto
rischio
rischio
cisti del plesso coroideo
Frequenza di anomalie cromosomiche
negli aborti spontanei (39.8%-40.9%)
•
•
•
•
•
trisomie autosomiche 49-52%
Turner (45, X) 15-19%
triploidia (69) 15-16%
tetraploidia (92) 5-6%
altre anomalie 6-14%
trisomia 21 Down
Il 70% delle
gravidanze
non giunge
a termine
1
1 2
2
1
1 2
2
1
1 2
2
1
1 2
2
1
1 2
2
1
1 2
2
1
1 2
2
1
1 2
2
Meiosis 1
error
Meiosis 1
1
1
1
1
2
1
1
2
+
2
1
Meiosis 2
1
1
or
1
SEA3069
1
1
1
1
2
1
2
1
2
2
or 3
other
combinations
+
2
2
Meiosis 2
error
Meiosis 2
1
1
1
Meiosis 1
Meiosis 1
or
other
combinations
+
1
1
1
1
Meiosis 2
2
Mitotic
error
2
1
1
2
2
origine dell’extra cromosoma 21
MM2
19.8%
MM1
68%
PM1
2.6%
PM2
4.1%
MIT
5.5%
Data from the Antonarakis and Hassold laboratories
sea3109
anomalie cromosomiche riscontrate
13
12
11.2
p
11.1
mosaicism
11.2
2
altre t
3
t21;22
21
17
t21;21
5
t15;21
q
6
t13;21
22.1
15
t14;21
925
free T21
1000
100
10
1
Numero
DSCR
Anomalia
11.1
27
D21S17
22.2
ETS2
22.3
MX1
HC21
Ipotesi sulla variabilità del fenotipo di 6 individui diversi in
caso di trisomia 21 in presenza di varianti alleliche
fenotipo
Livello di espressione
40.000 casi in Italia
trisomia 21 Down
Neurologici :
– Ritardo mentale
100%
– Alzheimer dopo i 35anni
100%
Ipotonia muscolare
100%
Bassa statura
70%
Testa :
– Brachicefalia
75%
– Epicanto
60%
– brushfield spots iride
55%
– lingua protrudente
45%
– orecchie displastiche
50%
trisomia 21 Down
Arti corti, mani larghe
65%
Mignolo corto
60%
Solco palmare trasverso
60%
Cuore
– Difetti cardiaci congeniti
40%
– Canale atrioventricolare
16%
Anomali gastrointestinali
– Atresia/stenosi duodenale
250x
– ano imperforato
50x
– Hirschsprung
300x
Sangue:
– Leucemia acuta megacariocitica
300x
– Leucemia (ALL e AML)
10-20x
trisomia 18 Edwards
•(1/6.500 nati)
•90% dei casi nondisgiunzione materna
•M/F = 1/4
•Giunge a termine solo il 2.5% dei
concepimenti
•Di questi il 33% muore nel primo mese,
il 50% entro 2 mesi
•Oltre 100 anomalie
•Peso sotto la norma, difficoltà suzione
•Ipotonia
•Idrocefalo, epilessia
•Malformazioni cardiache
•sinclinodattilia, unghie poco sviluppate
•piedi a calcagno prominente
•Gambe incrociate
trisomia 13 Patau
http://www.livingwithtrisomy13.org
•(1/12.000-20.000 nati)
•90% dei casi nondisgiunzione materna
•Giunge a termine solo il 2.5% dei
concepimenti
•Di questi il 33% muore nel primo mese,
il 50% entro 2 mesi
•Peso sotto la norma, difficoltà suzione
•Oloprosencefalia, microcefalia
•Cecità e sordità
•Occhi che possono fondersi
•Labiopalatoschisi 80%
•epilessia
•Malformazioni cardiache
•sinclinodattilia
•piedi a calcagno prominente
XX o XY
• Il sesso maschile è determinato dalla presenza del
cromosoma Y
• Si sono evoluti meccanismi per compensare la
differenza di dosaggio genico del cromosoma X,
presente in 2 copie nelle femmine e in 1 copia nei
maschi
2 cromosomi X nelle donne,
1 solo negli uomini?
1.
2.
il cromosoma X raddoppia
l’espressione di tutti i geni
contenuti, cioè si produce
2 volte più RNA
nelle femmine uno dei due
cromosomi X è inattivato
casualmente in ciascuna
cellula allo stadio di
blastocisti
Il Klinefelter?
1.
2.
Nel Klinefelter (XXY) uno
dei due cromosomi X è
inattivato casualmente in
ciascuna cellula allo stadio
di blastocisti
Quindi il dosaggio sarebbe
mantenuto
Sindrome di Klinefelter (47,XXY)
1:900-1:600 maschi
• Il 50% delle gravidanze giunge a
termine
• Fenotipo maschile
• Caratteristiche principali:
• Statura alta
– Ipogonadismo, bassi livelli di
testosterone, mancata produzione di
spermatozoi (azoospermia) e quindi
sterilità
– Ginecomastia
– Sia l’intelligenza sia l’attesa di vita sono
quasi normali
Altre forme citogenetiche
• Ma ci sono anche Klinefeler 48,XXYY and
48,XXXY in 1 caso su 17,000 e 1 su 50,000
mnati maschi
• 49,XXXXY in 1 caso su 85,000 -100,000
• Ci sono maschi 46,XX in cui avviene una
traslocazione di parte di cromosoma Y sul
cromosoma X che include la sex determining
region (SRY)
• mosaici
Le regioni PAR presenti sui cromosomi sessuali
contengono geni che non sono inattivati, perché il
doppio dosaggio è assicurato comunque
PAR1 ha 24 geni, PAR2 ha solo 4 geni
Il gene SHOX
Short stature HOmeoboX-containing
• Mutazioni o delezioni del gene SHOX nella
regione PAR1 causa ritardo di crescita e bassa
statura.
• La bassa statura di donne con sindrome di
Turner Syndrome (X0) è il risultato di una sola
copia di SHOX (ma anche il quarto metacarpo
corto)
• La maggiore statura nel Klinefelter (XXY) e nella
tripla X (XXX) potrebbe essere il risultato di 3
copie di SHOX
variabilità dei geni del cromosoma X delle regioni
PAR, quindi non inattivati
3 copie nel Klinefelter, ma anche nella tripla X
Mario Rossi
Luca Bianchi
Pio Verdi
Giulio Rosa
Lucio Viola
Gianni Neri
Livello di espressione
A complicare le cose…
• circa il 15 % dei geni umani presenti sull’X
sfugge all’inattivazione, mentre nel topo
questa è un’evenienza rara (solo 6 geni in tutto)
• alcuni sono espressi al 50-100% altri al 10%
• questo fenomeno è quindi incompleto e le donne
hanno una elevata eterogeneità nell’espressione
di geni dell’X
ipotesi sulla variabilità di ogni singola manifestazione
clinica di Klinefelter in presenza di varianti in geni del
cromosoma X non inattivati
Manifestazione clinica: NO
Mario Rossi
Luca Bianchi
Pio Verdi
Giulio Rosa
Lucio Viola
Gianni Neri
Livello di espressione
Manifestazione clinica: SI
Quanti Klinefelter?
• Prevalenza di XXYs è cresciuta da 1.09 a 1.72 per 1000
maschi nati (P=0.023)
• Questo incremento non è dovuto all’aumento dell’età
materna
• Sono nati 290.330 maschi in Italia e 31.573 maschi in
Campania nel 2007
• max 300-500 nuovi Klinefelter ogni anno in Italia (32-52
in Campania)
• XXY è la sola trisomia nota in cui circa il 50% dei casi è
causato da una non disgiunzione alla prima divisione
meiotica paterna
Trisomia X (47,XXX)
1:1.200
• Il 70% delle gravidanze giunge a termine
• Errore nella disgiunzione materna e
correla con l’età materna
• Caratteristiche principali:
– Statura alta
– Fertilità normale, irregolarità ciclo
– Sia l’intelligenza sia l’attesa di vita sono
normali
Maschio (47,XYY)
1:1.000 maschi
• Fenotipo maschile
• Caratteristiche principali:
– Statura alta
– Fertilità normale
– Non vi è correlazione con l’età paterna
– Sia l’intelligenza sia l’attesa di vita sono
perfettamente normali
Monosomia X (45,X0) Turner
Prende il nome dall’endocrinologo Henry
Turner che la descrisse nel 1938
La sindrome di Turner (TS) definisce un
complesso fenotipo umano femminile,
dovuto a completa o parziale assenza del
secondo cromosoma sessuale
Dipende da un errore nella spermatogenesi
nell’80% dei casi e non correla con l’età dei
genitori
Un precedente figlio con TS non aumenta il
rischio riproduttivo previsto per una coppia di
pari età
Monosomia X (45,X0) Turner
È l’unica monosomia compatibile con la vita, ma
il 98% di tutti i feti monosomici TS va incontro
ad aborto spontaneo
L’incidenza negli aborti è circa il 7-10%, mentre
alla nascita è 1/2500 femmine.
Non è chiaro perché il cariotipo 45, X0 sia letale
in utero ed invece compatibile con la
sopravvivenza postnatale
La vera monosomia del cromosoma X è
responsabile del 45% dei casi TS; gli altri hanno
mosaicismo (45, X0/46, XX) e/o un anormale
cromosoma X o Y
Un basso livello di mosaicismo somatico Turner,
inferiore al 2%, è di normale riscontro nella
popolazione
Monosomia X (45,X0) Turner
“la menopausa precede il menarca”
Le ovaie sono allungate e formate da
tessuto stromale privo di follicoli:gli oociti
sono spesso andati in apoptosi prima dei 2
anni di vita
L’insufficienza ovarica prepuberale porta
ad amenorrea primaria, sterilità e carenza
di estrogeni
In meno del 10% dei casi, la pubertà può
verificarsi e sono possibili gravidanze con
un aumentato rischio di perdita fetale
Anche in rapporto all’eterogeneità del
genotipo, il fenotipo si manifesta in modo
molto variabile
Monosomia X (45,X0)
Turner 1:2.500
• patologie dell’orecchio medio (otite media
ricorrente)
• Linfedema con rigonfiamento delle mani e dei
piedi
• pterigio del collo (presenza di pliche cutanee con
• aspetto di sfinge)
• il quarto metacarpo (anulare) più corto
• una mandibola più piccola (micrognazia)
• torace largo con aumento degli
• spazi intercostali
• l’attaccatura bassa delle orecchie e dei capelli
• Si possono anche riscontrare cardiopatia sinistra
(valvola aortica dicuspide, coartazione aortica),
ipertensione e anomalie renali
feto con anomalia cromosomica
(mosaicismo)
•
•
•
•
trisomie a mosaico 8, 9, 13, 18, 21
crescita in coltura di cellule materne
mosaicismo vero (livello III)
pseudomosaicismo (livelli II e I)
triploidia
Frequenza alla nascita = 1/10.000
Frequenza negli aborti = 1/14
Cariotipo 69,XXY 57%
Cariotipo 69,XXX 40%
Cariotipo 69,XYY 3%
Tipo I, corredo sovrannumerario paterno
Feto microcefalico o normale
Placenta ingrossata
Tipo II, corredo sovrannumerario materno
Ritardo di crescita
Feto con macrocefalia relativa
Placenta poco sviluppata
Nati vivi
Basso peso
Asimmetria cranio-facciale e difetti di ossificazione del cranio
Microftalmia, ipertelorismo, micrognazia
Sindattilia cutanea, piedi torti
Anomalie genitali, ipoplasia delle surrenali
Cardiopatie
Mosaicismo, quando il cambiamento avviene dopo
che si è formato lo zigote
47,XXY/46,XY
Un precedente figlio con anomalie
cromosomiche
Aumenta il rischio in caso di:
• tutte le trisomie non mosaico
• riarrangiamenti strutturali
• marker cromosomi
Un precedente figlio con anomalie
cromosomiche
NON aumenta il rischio in caso di:
• 47, XYY
• triploidia, tetraploidia
• sindrome di Turner
Valutazione del rischio riproduttivo nel
periodo preconcezionale
momento ottimale (ma oltre la metà delle gestazioni insorge
inaspettatamente)
raccolta dei dati (visita, abitudini, terapie, accertamenti lab)
• SCOPO: identificazione dei portatori sani di malattie genetiche
– portatori che hanno un rischio riproduttivo a prescindere dal
partner
– portatori in cui il rischio si manifesta solo nel caso di unione con
un partner portatore
portatori che hanno un rischio
riproduttivo a prescindere dal partner
• donne con
mutazioni legate
all’X (esempio:
Distrofia muscolare
di Duchenne)
portatori che hanno un rischio
riproduttivo a prescindere dal partner
• mutazioni dominanti ad esordio tardivo (corea di
Huntington, atassie spinocerebellari)
• mutazioni dominanti a penetranza incompleta
portatori in cui il rischio si manifesta
solo nel caso di unione con un altro
portatore
• mutazioni autosomiche recessive
– con familiarità (coppia già a rischio)
– senza familiarità (valutare la consanguineità)
ogni individuo è portatore sano di almeno
8 malattie genetiche recessive,
di cui 3 letali
•
•
•
•
fratelli, genitori-figli
fratellastri, zii-nipoti
cugini diretti (0.5%)
secondi cugini
•
•
•
•
1/4 omozigosi
1/8 omozigosi
1/16 omozigosi
1/64 omozigosi
i difetti congeniti hanno un rischio
empirico raddoppiato in caso di cugini
primi
non è utile l’esame cromosomico
portatori di un rischio riproduttivo indipendente dal partner
• portatori di una traslocazione
cromosomica bilanciata (reciproca)
• scambio di materiale genetico tra
cromosomi non omologhi
• non vi è modificazione della dose
genica
• frequenza 1/520 nati
• fenotipicamente normale
traslocazione reciproca
traslocazioni bilanciate
• lo scambio di segmenti cromosomici
avviene senza perdita di alcuna
informazione genetica
• nessuna regione cromosomica è
assente, ma è solo trasferita su un altro
cromosoma
• ma un gene di fusione tra due geni
altrimenti separati, un evento che è
comune nelle cellule maligne
traslocazione reciproca
traslocazioni bilanciate (meiosi e fertilizzazione)
Segregazione
alternata
Traslocazione
bilanciata
Normale
Traslocazione
Segregazione
adiacente 1
Traslocazione
Trisomia
Segregazione
adiacente 2
Trisomia
La formazione di tetravalenti aiuta a capire: solo con la segregazione alternata si
formano gameti normali o con traslocazione bilanciata, mentre le segregazioni
adiacenti 1 e 2 portano alla traslocazione sbilanciata o alla trisomia
traslocazioni robertsoniane (rob)
rob
• coinvolgono i cromosomi acrocentrici 13, 14,
15, 21 e 22
• nessuna regione cromosomica è assente,
perché questi contengono un braccio corto
privo di geni che può risultare perduto con la
fusione dei bracci q di due cromosomi
acrocentrici
• La più frequente traslocazione Robertsoniana
è la rob(13q14q) che rappresenta il 75% di
tutte le rob
• segue poi la rob(14q21q) e la rob(21q21q)
• si formano in genere durante la meiosi
femminile e comportano infertilità maschile o
abortività ripetuta.
Percentuale alla nascita di figli con cariotipo
sbilanciato da genitori con traslocazione
robertsoniana
•
•
•
•
t(13;14) M=F 1%
t(14;21) F 15% M 2%
t(21;22) F 10% M 5%
t(21;21) M=F 100%
Traslocazione sbilanciata
• maggiori sono le dimensioni cromosomiche, minore è la
possibilità di una gravidanza a termine
• minori sono le dimensioni, maggiore è il rischio di un feto
malformato
• Sesso del genitore donna>uomo (gli spermatozoi hanno
il 7.5% di difetti contro l’1% degli oociti, ma sono
selezionati)
• Il rischio aumenta se il difetto è stato accertato a partire
da un figlio precedente con cariotipo sbilanciato
rischio alla nascita di figli con cariotipo sbilanciato
• Se non vi sono stati casi in famiglia e la madre è
eterozigote per una traslocazione reciproca il rischio è il
7%
• Se non vi sono stati casi in famiglia e il padre è
eterozigote per una traslocazione reciproca il rischio è il
3%
• Se vi sono stati casi di traslocazioni sbilanciate in
famiglia e la madre è eterozigote il rischio è il 14%
• Se vi sono stati casi di traslocazioni sbilanciate in
famiglia e il padre è eterozigote il rischio è l’8%
inversioni
• Le inversioni sono rare (meno di 1 caso su 1000) e a
volte difficili da mettere in evidenza
• Possono essere semplici quando comprendono due
punti di rottura su di un singolo cromosoma
• Sono pericentriche quando il segmento invertito contiene
il centromero (es: 46, XX inv(3)p25q21)
• Le inversioni pericentriche dei cromosomi 1, 9, 16 e Y
sono eteromorfismi citogenetici di normale riscontro in
soggetti sani
• Le inversioni sono dette paracentriche se confinate ad
uno dei due bracci (es: 46,XX. Inv(11)q21q23)
• L’eterozigote per un’inversione è un soggetto normale.
coppia con familiarità per anomalie cromosomiche è
indicazione all’esecuzione di un cariotipo fetale e
l’estensione dell’indagine ai parenti
• traslocazioni X-autosoma
– maschi sterili, femmine inattivano la X
normale
• traslocazioni robertsoniane
– non 21 60% cariotipo bilanciato
– 21 15% rischio di Down, se è
eterozigote la madre 1% se è
eterozigote il padre
• inversioni
– pericentriche varianti dell’1, 9, 16 e Y, in
altri casi il rischio è 5-10%
– paracentriche, rischi inferiore allo 0.5%
donna eterozigote per una traslocazione bilanciata
X-autosoma
disordine genomico submicroscopico
un disordine genomico submicroscopico è una patologia
causata da
• acquisizione
• perdita
• alterazione
di uno o più geni contigui le cui variazioni di dosaggio
possono produrre effetti fenotipici
La base molecolare è rappresentata da
riarrangiamenti genomici, quali duplicazioni, delezioni,
inversioni, senza alterazioni apparenti del cariotipo (<5Mb)
FISH
Sonde FISH
le sonde FISH devono essere mirate, non possono essere utili
nell’analisi genomica generale
telomero
centromero
intero
cromosoma
locus
FISH
dominanza e recessività
• in genetica, il carattere (o l’allele) è dominante se
l’eterozigote è indistinguibile dall’omozigote
• in medicina la malattia è:
– dominante: fenotipo clinicamente manifesto
con 1 allele mutato
– recessiva: fenotipo clinicamente manifesto
con 2 alleli mutati (omozigote o eterozigote
composto)
La maggior parte dei geni autosomici si trova nella condizione A o C: il
dosaggio genico critico è <50%. In tal caso, si osserva un fenotipo
patologico solo se entrambi gli alleli sono colpiti
I geni autosomici responsabili della patogenesi dei disordini genomici si
trovano nella condizione B o D: si osserva un fenotipo già in eterozigosi
per aploinsufficienza. Spesso anche un dosaggio genico aumentato
>>100% può determinare una patologia
aploinsufficienza
• insufficiente quantità di prodotto genico causata da
una mutazione in eterozigosi
• la mutazione è di tipo allele amorfo o ipomorfo
• colpisce geni per i quali il 50% di prodotto genico
non è abbastanza per garantirne la funzione
• spesso un dosaggio preciso è richiesto ai fattori di
trascrizione e alle molecole di segnale espressi nel
corso dello sviluppo
In caso di delezioni del cromosoma X nei maschi si osserva direttamente in fenotipo
come sindrome da geni contigui
In caso di delezioni autosomiche in eterozigosi, molto spesso il dosaggio dimezzato
non è causa di malattia. Quando si osserva una sindrome da delezione, è risolutivo
trovare la stessa sindrome causata da una mutazione puntiforme in uno solo dei
geni. Se questa non si trova, la sindrome esiste solo come somma di più difetti.
ACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATA
GCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTC
CGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGC
TAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGC
GACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACAC
AGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTA
GCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACA
CACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCG
CACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCT
CTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACCGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGAT
ATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGAACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGC
TCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGAC
GTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGC
GCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGA
CCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGG
CTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCC
TGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGAC
CTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCG
ATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCAC
ACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTC
GAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATAT
ATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCT
CGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGA
GACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATAT
AGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACA
CCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCG
AGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATA
TAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTC
GAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGT
AGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGACGAGA
CGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAG
CGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAG
ACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGG
GCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCC
CTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCG
CTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGATAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCT
AGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCT
AGCTAGCTCCTCTCGACGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTC
GCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACC
GCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACC
GCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGACGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTC
GAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGA
AACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGA
AACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGACGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGAC
CTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGAC
ACACACAGATATTATAGCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGACGAG
ACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATA
GCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACA
CGTGCTAGCTAGCTCCTCTCGAGACGTTATAGCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTA
GCTCCTCTCGACGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGAC
ACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCG
AGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGC
ACACCGCTCGAGATAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCT
CGATATAGCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGACGAGACGTAGGGC
TCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCT
GAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGC
TAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGC
TAGCTCCTCTCGACGAGACGTAGGGCTCTCGATATAGCTCGCCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACAC
GTGCTAGCTAGCTCCTCTCGACGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACAC
AGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTA
GCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACA
CACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCG
CACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCT
CTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGA
ACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATA
GCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTC
CGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGC
TAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGC
GACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACAC
AGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTA
GCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACA
CACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCG
CACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCT
CTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACCGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGAT
ATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGAACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGC
TCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGAC
GTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGC
GCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGA
CCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGG
CTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCC
TGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGAC
CTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCG
ATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCAC
ACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTC
GAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATAT
ATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCT
CGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGA
GACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATAT
AGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACA
CCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCG
AGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATA
TAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTC
GAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGT
AGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGACGAGA
CGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAG
CGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACTATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACCGAGACGTAGGGCTCTCGATATA
GCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTC
CGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGC
TAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGC
GACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCG
ACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTA
GCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGCGAGACGTAGGGCTCTCGATATAG
CTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCC
GACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCT
AGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCG
ACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACA
GCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACA
GCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGACGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGC
TAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACA
CACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCT
CGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTC
CTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACA
GATATATAGCGGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGATAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCT
CCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCT
CCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGACGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGA
CCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCT
CGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCT
CGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGACGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTC
CGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTTAGCTAGCTCCTCT
CGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATA
TATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGACGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAG
ATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACAC
CGCTCGAGACCTTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATTATAGCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACAC
AGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGACGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAG
CTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATAT
AGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTTATAGCTCGCGACACACACAGATATATAGCGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTG
AAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGACCTGACACGTGCTAGCTAGCTCCTCTCGACGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTGA
CCTGACACGTGCTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGACACACACAGATATATAGCGCTCCCTGAAACAGCTCCGACACAGCTCGCACACCGCTCGAGACCTTAGCTAGCTCCTCTCGAGACGTAGGGCTCTCGATATAGCTCGCGA
Copy Number Variation
10% of the human genome could vary in copy number
1
2
duplicazioni segmentali
• il genoma umano contiene complessivamente il 13,7% di
segmenti duplicati con almeno il 90% di identità di sequenza
• il 5,2% del genoma contiene segmenti duplicati lunghi tra 1 e
10kb, mentre il 4,5% tra 10kb e 20kb
• i cromosomi più colpiti sono l’Y (50,4%) ed il 22 (11,9%), ma
anche il 7, 9, 10, 15, 16, 17 e X
• le duplicazioni segmentali possono essere intracromosomiche
o intercromosomiche
• con tre localizzazioni differenti:
– pericentromeriche (47Mb, dupliconi originati da altri cromosomi)
– subtelomeriche (ciascuna solo 50-100kb, orientate)
– interstiziali (solo nella specie umana sono disseminate ad una
distanza media di 3Mb)
Malattie autosomiche dominanti
Come fanno le delezioni in uno solo dei due alleli a
costituire un carattere dominante?
1. il livello dimezzato di prodotto genico è insufficiente
a mantenere il fenotipo
2. il difetto eterozigote diviene omozigote a livello
delle cellule dei tessuti periferici (LOH)
3. un solo allele è espresso per imprinting dell’altro
principali sindromi da delezione
LOCALIZZAZIONE
CROMOSOMICA
SOGGETTI CON
MICRODELEZIONE
Prader Willi/Angelman
15q11.13
70%
Williams
7q11.23
90%
DiGeorge/Velocardiofacciale
22q11.2
75%
Smith-Magenis
17p11.2
95%
Miller-Dieker
17p13.3
90%
SINDROME
Sindrome di DiGeorge
DiGeorge/velocardiofacciale
La sindrome di DiGeorge del22q11.2 è la più frequente sindrome da
microdelezione, con un incidenza di 1 su 4000—5000 nati
La delezione comprende 3Mb ed almeno 30 geni
• Migrating neural crest cells
make a contribution to the
embryonic structures affected
in DiGeorge syndrome.
• The cartoon represents a
human embryo at 4–6 weeks
gestation.
• The migration of neural crest
cells from the hindbrain to the
branchial arch/pharyngeal
pouch system and cardiac
outflow tract is indicated by
the arrows.
• Examples of malformations
associated with perturbation
of this process are listed and
these overlap substantially
with those seen in 22q11DS
AAA, arch arteries; PDA,
persistent ductus arteriosus;
IAA, interrupted aortic arch.
DiGeorge
• È caratterizzata da
– Anomalie cardiache
– T-cell deficit
– palatoschisi
– anomalie facciali
– Ipocalcemia
Mutazioni puntiformi del gene TBX1 possono portare a questi 5 tratti
fenotipici, ma non alle difficoltà nell’apprendimento che è invece
frequente nella sindrome da delezione
Williams-Beuren
• prevalenza alla nascita 1/75001/20.000, ma può non essere
diagnosticata
Williams
una delezione tipica
Williams
genetica
• delezione “de novo”
• trasmissione autosomica dominante
• delezione di 1.6MB da 21 geni contigui in eterozigosi a
7q11.23
– gene dell’elastina
– LIM kinase 1 (LIMK1)
– CLIP-115 che lega i microtubuli
– Fattori di trascrizione GTF2I e GTF2IRD1
– effetto posizionale su altri geni circostanti la
delezione
Williams
FISH delezione 7q11.23
rilevabile
mediante FISH ma non cariotipo
Williams
comportamento
• lieve o medio ritardo mentale (IQ tra 41 e 80)
• scarsa capacità di concentrazione
• ritardo nell’apprendimento del linguaggio e poi
esagerata loquacità
• personalità amichevole e affettuosa
• danno facilmente confidenza anche a sconosciuti
• ansietà, spesso preoccupati per il benessere altrui
• ipersensibilità ai suoni
• memoria visiva e uditiva spesso fuori dal comune
• ricordano persone, luoghi e motivi musicali
• predisposizione ad imparare le lingue e la musica
Williams
aspetto e segni
• Faccia da elfo
• Occhi blu (77%) con pattern stellato dell’iride (74%)
ma questo vale per i nordeuropei, strabismo (40%)
• Naso con la punta bulbosa
• bocca larga e guance piene
• microdontia e micrognazia
• Statura 10 cm in meno del normale
• ipercalcemia
• stenosi periferica delle arterie polmonari
• stenosi aortica sopravalvolare
http://www.wsf.org/family/photoalbum/wsfphoto.htm
Williams
foto
Williams foto
Wolf-Hirschhorn
genetica
• delezione “de novo” di circa 4MB
• le delezioni sono più frequenti nella linea
germinale maschile
• trasmissione autosomica dominante
• Regione critica di 165 kb di molti geni
contigui in eterozigosi a 4p16.3
Wolf-Hirschhorn
delezione a 4p16.3
Wolf-Hirschhorn
•
•
•
•
Scarso accrescimento
Ritardo mentale, ipotonia
Labbro leporino
Conformazione ad elmo di
guerriero greco
Sindrome 5p- (cri du chat)
1:50.000 nati
• Pianto acuto e flebile
• Caratteristiche principali:
– Ritardo di crescita
– Microcefalia ed ipertelorismo
– Ipotonia, diastasi dei retti
– Deficit intellettivo e del linguaggio
Imprinting
Imprinting
• Nelle cellule germinali primordiali l’imprinting viene
cancellato del tutto e il DNA è demetilato
• Successivamente nella linea germinale maschile si
determina un pattern di imprinting che in alcuni loci è
complementare a quello della linea germinale femminile
• I cromosomi su cui avviene l’imprinting (7, 11, 15)
manterranno questo pattern e lo riprodurranno ad ogni
mitosi
• Si potranno sempre distinguere l’espressione genica del
cromosoma materno e paterno
Disomia uniparentale
• Due copie dello stesso cromosoma sono
ereditate dallo stesso genitore
• Spesso questo avviene attraverso un
fenomeno transitorio di trisomia, seguito
dalla perdita del cromosoma singolo e
mantenimento del cromosoma doppio
Angelman
• 70% dei casi delezione della regione cromosomica
15q11-q13, che è soggetta al fenomeno dell'imprinting
del cromosoma paterno
• Il gene materno (l'unico espresso) può essere alterato
con 4 meccanismi noti:
–
–
–
–
delezione
disomia uniparentale paterna
difetti nell'imprinting
mutazioni a carico del gene UBE3A (ubiquitin ligasi)
• La diagnosi è clinica e il difetto genetico non si identifica
nel 20% dei casi
Angelman
• "happy puppet syndrome" si
può identificare in Cucciolo
(Dopey) "addormentato", il
più giovane dei nani che non
ha mai imparato a parlare
• ritardo mentale con assenza
del linguaggio, difficoltà
nell'equilibrio, eccessivo
buon umore
Angelman
• L'incidenza è 1/20.000
nati
• crisi epilettiche e
comunque alterazioni
dell'EEG e microcefalia
relativa
Prader-Willi
•
•
•
•
•
•
iperfagia>obesità
eccessiva assunzione di liquidi
reazioni abnormi ai sedativi
acromicria, criptorchidismo
insensibilità al dolore, lesioni cutanee
sbalzi di umore
Prader-Willi
1/15.000
Nomenclatura delle delezioni
• Le delezioni sono designate con la sigla del che segue i
numeri dei nucleotidi a monte e a valle della delezione
separatida un segno _
– 82_83del (o 82_83delTG) indica una
delezione di TG nella sequenza
ACTTTGTGCC (dove A è il nucleotide 76) che
diventa ACTTTGCC
Cosa sono le distrofie muscolari?
• Malattie degenerative
progressive
• Variazione dello spessore delle
miofibrille con forti cambiamenti
nella istologia del muscolo
• indebolimento e degenerazione
del tessuto muscolare in fibroso
e adiposo
• aree di necrosi con processi
infiammatori
Duchenne
Becker
EmeryDreifuss
facioscapoloomerale
cingoli
distale
oculofaringea
Distrofia muscolare
Duchenne/Becker
DMD Duchenne - 1/3,500 maschi
• Insorgenza -- Infanzia - tra 2 e 6 anni
• Sintomi – Debolezza generalizzata e danno muscolare
prima agli arti e al tronco, polpacci ingrossati
• Progressione – Lenta ma inesorabile. Colpisce tutti i
muscoli volontari. Sopravvivenza fino a 25-30 anni
BMD Becker - 1/10,000 maschi
• Insorgenza – Adolescenza o dopo
• Sintomi – Identici alla DMD ma più attenuati. Vi è
coinvolgimento cardiaco significativo
• Progressione – Più lenta e più variabile della distrofia di
Duchenne con buona aspettativa di vita
Le delezioni intrageniche del gene della distrofina mandano fuori
cornice la lettura delle triplette quando gli esoni cancellati
contenevano un numero di nucleotidi che non è multiplo esatto di
tre (1,2,4,5,7,8,10,11 ecc). Questo causa la distrofia di Duchenne.
Le delezioni intrageniche che non alterano la cornice di lettura
portano alla distrofia muscolare di Becker o ad un apparente
buona salute. Forniscono informazioni per preparare delle
microdistrofine per la terapia genica
Nomenclatura delle delezioni
• Le delezioni sono designate con la sigla del che segue i
numeri dei nucleotidi a monte e a valle della delezione
separatida un segno _
– 82_83del (o 82_83delTG) indica una
delezione di TG nella sequenza
ACTTTGTGCC (dove A è il nucleotide 76) che
diventa ACTTTGCC
La tecnica del CGH (comparative
genomic hybridization) permette
l’individuazione di sequenze
delete o duplicate nel genoma da
testare (red) mediante il confronto
con un genoma di riferimento
(green).
Sono preparate due sonde
fluorescenti di colore diverso che
ibridano contemporaneamente sui
cromosomi. Se in una regione
cromosomica prevale il colore
(green) relativo al genoma di
controllo questo significa che il
genoma da testare (red) ha una
delezione in quella regione
classificazione funzionale delle mutazioni
1. allele equivalente
2. allele ipomorfo
3. allele amorfo
4. allele ipermorfo
5. allele neomorfo
6. allele antimorfo
1. allele equivalente
• variazione che non modificano né la quantità, né la
qualità biochimica e funzionale del prodotto genico
• il prodotto genico risulta invariato e normalmente
localizzato
• esempi sono le circa 12,000 differenze della
sequenza del DNA codificante che si osservano nella
popolazione umana che non hanno alcuna
conseguenza patologica
2. allele ipomorfo
• variazione della sequenza del DNA che riduce la quantità di
prodotto genico e/o la sua qualità funzionale
• tali alleli sono silenti e recessivi e possono agire più come
modificatori del fenotipo che come causa diretta di patologia
• alleli ipomorfi possono però essere causa di malattia se in
emizigosi
• esempio: gli alleli ipomorfi del gene della distrofina localizzato
sul cromosoma X che determinano quadri di distrofia muscolare
di Becker nei maschi in quanto hanno una singola copia del
gene
3. allele amorfo
• variazione di sequenza del DNA più drastica: corrisponde
classicamente alla delezione (cancellazione) della sequenza
codificante del gene
• un allele amorfo può essere prodotto da altri tipi di mutazione che
abbiano la medesima conseguenza di una delezione totale del
gene
• causa in emizigosi una malattia genetica quando colpisce una
funzione genica essenziale (es emofilia, distrofia muscolare di
Duchenne, ecc)
• l’allele amorfo in eterozigosi in genere è presente in un portatore
sano di una malattia autosomica recessiva
• può da solo essere causa di malattia se riguarda un gene in cui il
50% del dosaggio (prodotto dall’altro allele non mutato) è
insufficiente a mantenere lo stato di salute (aploinsufficienza)
4. allele ipermorfo
• ipermorfo (iper= aumentato) è l’allele che determina l’aumentata
quantità o funzione di un prodotto genico
• l’allele ipermorfo può essere semplice o avere una combinazione
di altri effetti come ad esempio, quello di essere presente in una
localizzazione impropria o in un tempo sbagliato
• è associato di regola ad un tratto genetico dominante, in quanto
l’aumentata espressione/funzione non può essere limitata
dall’allele non mutato
• un esempio è l’aumentata funzione del recettore per l’FGF3 che
causa l’acondroplasia (nanismo dismorfico) che è appunto a
trasmissione autosomica dominante
5. allele neomorfo
• neomorfo (neo=nuovo) definito come causato da una mutazione
che porta ad un prodotto genico nuovo o una funzione nuova
• si distingue solo didatticamente dall’allele ipermorfo, in quanto è
in pratica una variante che è difficile da distinguere nelle singole
condizioni
• valgono le stesse considerazioni fatte per l’allele ipermorfo sulla
natura dominante della mutazione
• in alcune forme di cancro l’allele neomorfo è una chimera di due
geni, dovuta ad una traslocazione cromosomica, come il
cromosoma di fusione Philadelphia con la comparsa di nuove
proteine Bcr-abl in casi di leucemia mieloide cronica
6. allele antimorfo o dominante negativo
• antimorfo (anti=contro) definito come causato da una mutazione
che porta ad un prodotto genico antagonistico
• è il risultato di una mutazione che colpisce un gene il cui prodotto
proteico funziona in cooperazione con altre proteine
• particolari mutazioni rendono la proteina di disturbo a tutte le altre
pur essendo queste ultime perfettamente normali
• un esempio è dato dal collageno in cui più geni (e due alleli per
ogni gene) contribuiscono alla formazione delle proteine ciascuno
producendo una parte delle catene di base: una mutazione in un
solo allele produce un effetto negativo complessivo
classificazione strutturale delle mutazioni
1.
sostituzioni
2.
piccole inserzioni, delezioni o inserzioni +
delezioni contemporaneamente (indels)
3.
riarrangiamenti genomici a due (delezioni,
duplicazioni) o più punti di rottura
(traslocazioni, inversioni ecc.)
4.
copy number variations (CNV)
a queste quattro classi appartengono in modo
indistinguibile tanto le variazioni innocue
quanto le mutazioni causative di malattia
mutazioni
I dati di sequenziamento totale del genoma provano che almeno
10-8 sostituzioni geniche per base si verificano nella prole de
novo, cioè senza essere ereditate dai genitori
tutte le nuove sostituzioni sono in eterozigosi o in emizigosi se si
verificano nei cromosomi sessuali maschili
le nuove sostituzioni possono produrre varianti private
meno dell’1% cadono negli esoni codificanti dei geni
•mutazioni silenti, quando l’aminoacido non cambia
•mutazioni missenso quando un aminoacido è sostituito da un
altro aminoacido
•mutazioni nonsenso quando un aminoacido è sostituito da un
codone prematuro di terminazione
•mutazioni nonstop quando al contrario un codone di terminazione
è sostituito da un codone di un aminoacido
Numerazione dei nucleotidi
Nucleotidi del cDNA
• Il nucleotide +1 è la A dell’ ATG-codone di inizio della
traduzione
• Il nucleotide che precede al 5' l’ATG-codone di inizio
della traduzione è denominato -1; non esiste una base 0
• Il nucleotide che segue al 3' il codone di terminazione è
denominato *1
sostituzioni
• le sostituzioni sono indicate dal carattere “>”. Ad
esempio, 76A>C indica che in posizione 76 un’adenina è
sostituita da una citosina
88+1G>T (oppure IVS2+1G>T) indica che una guanina è
sostituita da una timina in posizione +1 dell’introne 2,
posizionato tra i nucleotidi 88 e 89 del cDNA
89-2A>C (oppure IVS2-2A>C) indica che un’adenina è
sostituita da una citosina in posizione -2 dell’introne 2,
posizionato tra i nucleotidi 88 e 89 del cDNA
mutazioni
SNPs
teoricamente
previste
T>A o G , C>G or A
G>T o C , A>T or G
trasversioni
trasversioni
trasversioni
transizioni
transizioni
transizioni
T>C, C>T, G>A, A>G
46,000
12,000,000
SEA 3057
Il meccanismo più comune di mutazione
NH2
NH2
O
H3C
H3C
O
metilazione
O
deaminazione
5-methylcytosine
CG
CG
O
N
N
N
Cytosine
NH
N
N
TG
CA
Thymine
mutazioni puntiformi missenso
• Le mutazioni missenso sono quelle in cui il cambiamento
determina nel prodotto proteico la sostituzione di un
aminoacido con un aminoacido differente
• Sebbene queste alterazioni generalmente non
provochino conseguenze nella funzionalità della proteina
(polimorfismi o varianti) , ci sono casi in cui anche una
minima alterazione può avere conseguenze gravi
acrocefalosindattilia
sindrome di Apert
•1:65.000 alla nascita
•craniosinostosi, volta cranica a
forma conica
•ipertensione endocranica
•ritardo mentale
•ipoplasia della parte centrale
della faccia
•sindattilia delle dita delle mani e
dei piedi
•sordità e atrofia ottica
acrocefalosindattilia
sindrome di Apert
• tutti i pazienti hanno la stessa mutazione Apert
(Cys755Gly) del gene human fibroblast growth factor
receptor 2 (FGFR2)
• la mutazione è in eterozigosi
• de novo
• cromosoma 10q26
• la sindrome è allelica con Crouzon e Pfeiffer
sindrome di Pfeiffer
• alcuni pazienti hanno la mutazione Pfeiffer (Cys342Arg) del gene
human fibroblast growth factor receptor 2 (FGFR2)
• altri la mutazione Pro252Arg in FGFR1
• la mutazione è in eterozigosi
• de novo
• cromosoma 10q26
• la sindrome è allelica con Crouzon e Apert
disostosi cranio facciale
sindrome di Crouzon
• alcuni pazienti hanno la mutazione (Cys342Tyr) del gene
human fibroblast growth factor receptor 2 (FGFR2)
• la mutazione è in eterozigosi
• de novo
• cromosoma 10q26
• la sindrome è allelica con Pfeiffer e Apert con alcune
mutazioni in comune
acondroplasia
•
•
•
•
nanismo dismorfico (1:35.000)
arti corti e testa sproporzionatamente più grossa
fronte prominente e naso appiattito
altezza media 130 cm nei maschi 125 cm nelle
femmine
• La mutazione è in eterozigosi
• Gly380Arg nel recettore 3 del "fibroblast growth
factor" (FGFR3) a 4p16.3
• autosomico dominante a penetranza completa
acondroplasia
• La mutazione conferisce una funzione aumentata al
recettore dell'FGF (allele ipermorfo) che è una tirosinchinasi di membrana
• In risposta all'FGF il recettore dimerizza e si fosforila
trasducendo un segnale con la funzione di rallentare la
proliferazione dei condrociti e quindi la crescita ossea
• Topi senza il gene FGF3R hanno ossa lunghe e vertebre
allungate
frequenza relativa di mutazioni de novo
che causano acondroplasia i rapporto all’età paterna
numero di divisioni nelle linea germinale maschile
ipocondroplasia
•L'ipocondroplasia ha caratteristiche simili
all'acondroplasia, ma di gravità minore con un
coinvolgimento craniofacciale inferiore. L'altezza può
risultare ai limiti della norma e la malattia viene spesso
non diagnosticata.
•L'ipocondroplasia è meno omogenea: circa il 70% dei
casi è dovuto alla sostituzione N540K del gene FGFR3,
mentre non si conosce la mutazione nel restante 30%.
mutazioni puntiformi nonsenso
• La mutazione nonsenso è quella in cui la
modificazione nucleotidica provoca la
creazione di un tripletta di stop, che blocca
la sintesi della proteina prematuramente.
• In questo caso, la funzionalità della
proteina dipenderà dalla posizione dello
stop.
Mutazioni dei codoni umani
(mutazioni independenti nei geni F8, F9, L1CAM, OTC, BTK)
300
200
5082 Codons in 5 chrX genes
2446 Mutations in 5 chrX genes
Gly G
Arg R
Trp W
Cys C
Glu E
Asp D
Lys K
Asn N
Gln Q
His H
Tyr Y
Ala A
Thr T
Pro P
Ser S
Val V
Met M
Leu L
0
Ile I
100
Phe F
Numbers normalised to 1,000
400
mutazioni nonsenso
15%
16%
UAA
UAG
UGA
69%
Su 731
mutazioni independenti
SEA 3063
in 9 patologie del cromosoma
X
mutazioni frame-shift
• Le mutazioni frame-shift o di slittamento
del modulo di lettura consistono
nell’inserzione o delezione di un numero di
nucleotidi non divisibile per 3 (1, 2, 4, 5, 7,
8, 10, ecc.) con conseguente sfasamento
della cornice di lettura delle triplette
dell'RNA messaggero.
• Questa mutazione determina la traduzione
non corretta della proteina a valle della
mutazione.
mutazioni eterozigoti di PAX3
Waardenburg
mutazioni eterozigoti di PAX3
Waardenburg
• sordità (o deficit uditivo di vario livello) bilaterale,
• modifiche nella pigmentazione, sia dei capelli (albinismo
parziale, in genere piebaldismo) che della pelle,
• anomalie nello sviluppo dei tessuti derivati dalla cresta
neurale
• lateralizzazione del canto mediale
• diverso colore degli occhi (eterocromia), di solito uno
marrone e l'altro blu
Motivi classici di splicing
Nucleotidi intronici fiancheggianti
• inizio dell’introne: il numero dell’ultimo nucleotide
dell’esone che precede, il segno + e la posizione
nell’introne, ad esempio 77+1G, 77+2T, oppure quando il
numero dell’esone è noto ed univoco IVS1+1G, IVS1+2T
• fine dell’introne: il numero del primo nucleotide del
esone seguente, il segno – e la posizione a monte
dell’esone, ad esempio 78-2A, 78-1G, oppure quando il
numero dell’esone è noto ed univoco, IVS1-2A, IVS1-2G
HGMD Mutations in Intron splice sites
1000
1800
900
1600
2296 Acceptor
Splice Site mutations
800
(5Jan07)
3498 Donor
Splice Site mutations
1400
700
1200
600
1000
500
800
400
600
300
400
200
200
100
0
0
-15
-13
-11
-9
-7
-5
-3
-1
2
4
Nucleotide number in the acceptor site
-5
-3
-1
2
4
6
8
10
12
14
Nucleotide number in the donor site
exon
5’ss
3’ss
exon
IVS
5’ss mutation; exon skipping
3’ss mutation; exon skipping
5’ss mutation; use of cryptic 5’ss
3’ss mutation; use of cryptic 3’ss
Activation of cryptic 5’ss
Activation of cryptic 5’ss and use of cryptic 3’ss
Splicing enhancer mutation
Lariat structure branchpoint mutation
5’ss
3’ss
IVS
exon
Progeria
Hutchinson-Gilford
• invecchiamento precoce
• bassa statura, pelle rugosa
• calvizie, assenza di tessuto adiposo
• aterosclerosi ed infarto
Progeria
Hutchinson-Gilford
• nuova mutazione in eterozigosi del gene lamina A
• la mutazione è in eterozigosi
• de novo
• cromosoma 1q23
• La mutazione non cambia l'aminoacido glicina G608G,
ma introduce un sito donor di splicing GGT che fa
perdere 50 aminoacidi alla proteina
• sperimentazione con inibitori di farnesil-trasferasi
Malattie genetiche da mutazione in 1 allele
Le mutazioni monoalleliche possono causare disordini a
trasmissione dominante o recessiva legata all’X negli uomini
•
•
•
Se la malattia a trasmissione dominante è grave in età fertile e
pertanto limita o annulla la capacità riproduttiva (bassa fitness), le
mutazioni monoalleliche sono nuove e spesso distribuite in modo
casuale
Se la malattia dominante non è grave in età fertile e non limita in
alcun modo la capacità riproduttiva (normale fitness), le mutazioni
monoalleliche sono ereditate da un genitore e spesso si
tramandano da molte generazioni
Se la malattia è recessiva legata all’X ed è letale ha una vita media
di tre generazioni, perché le donne trasmettono gli alleli mutati in
eterozigosi e gli uomini li eliminano
eredità autosomica dominante a penetranza completa
(malattia che non modifica la fitness)
Cos’è una mutazione causativa?
Una variazione della sequenza del DNA ….
• ..che è trovata solo negli individui affetti
• ..che non è mai ritrovata in quelli non affetti
• ..che spiega il processo patologico
• ..che, quando corretta per tempo, fa recuperare un
fenotipo normale
….che è trovata solo negli individui affetti
..che non è mai ritrovata in quelli non affetti
penetranza incompleta
che è ritrovata più frequentemente negli
individui affetti rispetto ai non affetti…
Malattie genetiche da mutazione in 2 alleli
Le mutazioni bialleliche possono causare disordini a
trasmissione autosomica recessiva
•
•
•
Se la malattia a trasmissione recessiva è grave in età fertile e limita
o annulla la capacità riproduttiva (bassa fitness), le mutazioni non si
estinguono comunque perché i portatori sani sono 10-10.000 volte
più numerosi degli affetti
Le mutazioni in genere si trasmettono da 100-1000 generazioni,
mentre le nuove mutazioni sono rare
Solo se la malattia è biallelica le mutazioni hanno una firma etnica
che caratterizza una località di origine e un fondatore comune
eterozigote sano
Malattie da 2 alleli
• L’alto numero di portatori è un fattore di rischio per l’eterozigosi
composta (due mutazioni differente nei due alleli). Questo potrebbe
essere causato da una fitness migliore degli eterozigoti nei confronti
di un fattore negativo vedi A
• La consanguineità è un fattore di rischio per l’omozigosità (due alleli
identici) anche se la mutazione è rarissima vedi B
conversione genica